SOLUTION ソリューション
バイオ分子相互作用シミュレータMIZUHO/BioStation
概要
MIZUHO/BioStationは、フラグメント分子軌道(FMO)法プログラムMIZUHO/ABINIT-MPとその専用プリポストMIZUHO/BioStation Viewerから構成される量子化学計算ソフトウェアです。
当社では、MIZUHO/BioStationの販売から解析コンサルティング、カスタマイズまでのサービスの提供を通じ、創薬、バイオ、材料分野における分子設計を支援いたします。
MIZUHO/BioStationは、これまでに、インフルエンザウイルスの膜表面タンパク質における抗原抗体反応や抗ウイルス薬タミフルの酵素-阻害剤結合、生活習慣病や乳がんにかかわる核内受容体のリガンド結合や転写の分子メカニズム、肺がんの分子標的薬とのドッキング、DNA転写等、さまざまな分子認識における相互作用の解析を行った実績を有しています。 タンパク質、DNAなどの生体高分子への適用はもちろん、今後、ナノ材料分子への適用が期待されています。

MIZUHO/ABINIT-MPは、FMO法に基づく電子状態計算プログラムです。FMO法では、分子や分子の集合体を適当なサイズのフラグメント(断片)に分割し、必要に応じてフラグメントのモノマーからテトラマーまでの分子軌道(MO)計算を行い、分子全体のエネルギーや電子状態を計算します。低分子化合物で成功を収めた分子軌道計算を、精度を落とさずにタンパク質のような巨大分子へ適用することが出来ます。
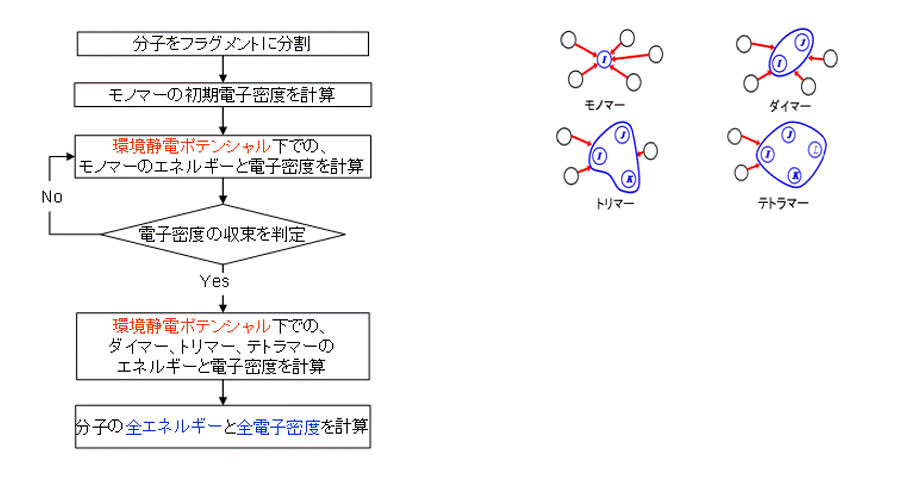
MIZUHO/BioStation Viewerは、MIZUHO/ABINIT-MPの入力ファイルの作成やフラグメント分割などのプリ処理から、フラグメント間相互作用エネルギー(IFIE)解析、軌道相互作用解析(CAFI, FILM)などのポスト処理までをサポートします。
* 「BioStation」、「ABINIT-MP」は、国立大学法人東京大学の登録商標です。
MIZUHO/BioStationの特徴
・FMO法を用いた大規模分子の電子状態計算および相互作用解析が可能
・MP2法を始めとする高次電子相関手法が利用可能
・フラグメント間相互作用、軌道相互作用、電荷分布等、FMO計算結果に対する充実した解析機能を搭載
・FMO4計算に基づく4体補正まで考慮したフラグメント間相互作用解析が可能
・IFIEを各エネルギー成分に分解して解析できる「PIEDA」を搭載
・フラグメント分割等の入力処理をGUIによりサポート
MIZUHO/BioStationの機能概要
(1)フラグメント分割機能および入力ファイルの作成
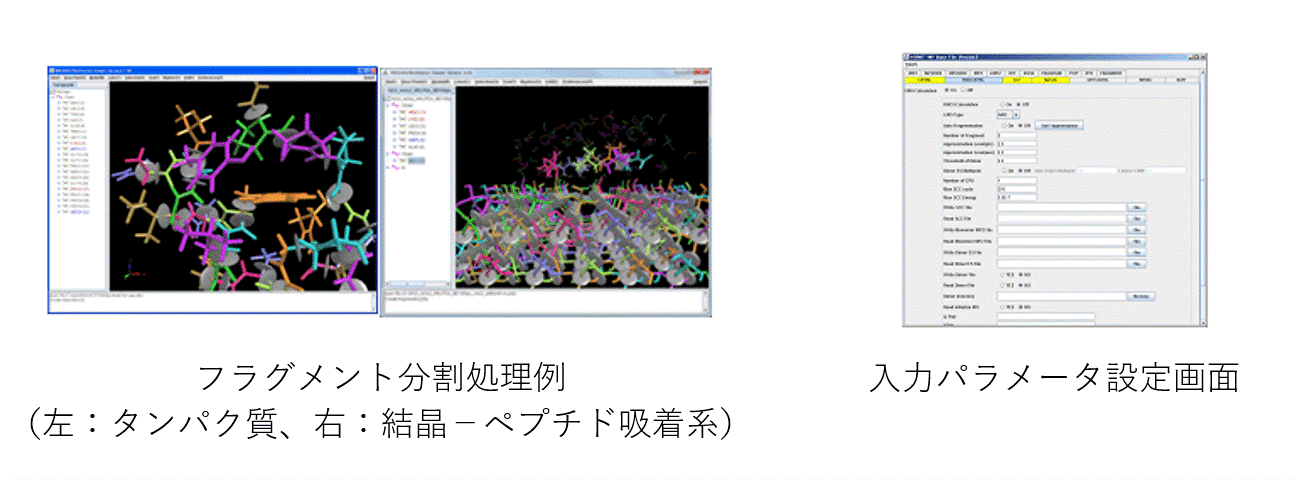
MIZUHO/BioStation Viewerでは、FMO計算のためのプリ機能として、タンパク質、DNAの自動分割はもちろん、マニュアル操作による手動分割を行うことができる機能を有しています。フラグメント分割機能は、医薬品候補化合物など、多様な化学構造に対応しており、GUI画面上で作成した構造について、MIZUHO/ABINIT-MPの入力ファイルの作成も行うことができます。
(2)CH/π相互作用解析
MIZUHO/BioStation Viewerでは、CHPI プログラム(*)を用いてCH/π相互作用に対する構造解析を行うことができます。タンパク質や、タンパク質ーリガンド複合体の入力構造に対して、分子内や分子間に存在するCH/π相互作用の有無を検索して立体構造画面上に表示することができます。
* CHPI プログラムは、微生物化学研究所 梅沢洋二先生、CHPI研究所の西尾元宏先生、および微生物化学研究会によって開発されたソフトウェアです。
(3)フラグメント間相互作用エネルギー(IFIE)解析
MIZUHO/BioStationの大きな特徴として、FMO計算の実行により、IFIEと呼ばれる各フラグメント間の相互作用エネルギー値を得ることが挙げられます。IFIEを用いて、タンパク質と化合物、タンパク質とタンパク質、DNAとタンパク質、等の分子間相互作用を可視化・解析することが可能となります。例えば受容体ータンパク質系では、タンパク質の各アミノ酸残基とリガンドとの相互作用エネルギーを定量的に見積もることにより、ドッキング構造の量子化学的な評価、アミノ酸残基の変異による結合能の変化などリガンドの結合特性を定量的に評価・予測することができます。さらに、網羅的な2体相互作用解析を行うことのできるIFIE mapや、複数の化合物に対する相互作用パターンの抽出と化合物のクラスター分類(VISCANA)など、IFIEに基づいた様々な解析機能を搭載しています。

(4)PIEDA解析
PIEDAは、北浦-諸熊のエネルギー分割法をFMOに適用し、相互作用エネルギーを各成分(静電項、交換反発項、電荷移動項、分散項)に分解して解析する手法です。タンパク質と医薬品候補化合物との相互作用をデザインする際に、相互作用の性質を理解して論理的な創薬に結びつけることができます。MIZUHO/BioStationでは、PIEDA成分を可視化しながら解析することができます。
(5)軌道相互作用解析(CAFI、FILM)
MIZUHO/BioStation Viewerでは、軌道相互作用解析として、水素結合などにおける電荷移動相互作用の解析ツールCAFI(Configuration Analysis for Fragment Interaction)や、CH/πやπ/πなど分散相互作用の解析ツール、FILM (Fragment interaction based on local MP2)の計算結果に対する可視化解析機能を有しています。この機能を用いることで、エネルギー解析よりも詳細な軌道相互作用を評価することができます。

(6)グリッドデータ解析
MIZUHO/BioStationでは、cpf2denモジュールを用いて、分子のグリッドデータを解析することができます。電子密度分布や静電ポテンシャル、フラグメントの分子軌道(MO)などを可視化することが可能です。タンパク質表面の静電ポテンシャルマップなどを描画することができ、静電相互作用による分子認識の解釈などに役立ちます。

過去のニュース
・ABINIT-MPが2011年6月20日の日本経済新聞朝刊で紹介されました。
「新薬設計の精度5倍に 立教大などがスパコン新ソフト」
・ABINIT-MPが2011年6月21日の日経産業新聞で紹介されました。
「スパコンで創薬設計 みずほリサーチ&テクノロジーズなどソフト」
・ABINIT-MPが2011年9月13日の日経産業新聞で紹介されました。
「スパコン創薬『京』の号砲」
「イノベーション基盤シミュレーションソフトウェアの研究開発」プロジェクト
・ABINIT-MPおよびBioStaion Viewerは、文部科学省次世代IT基盤構築のための研究開発「イノベーション基盤シミュレーションソフトウェアの研究開発」プロジェクト(http://www.ciss.iis.u-tokyo.ac.jp/)において開発されています。
・弊社ではABINIT-MPおよびBioStation Viewerの開発の一部とこれらを用いた応用計算を担当しております。
・弊社ではABINIT-MPおよびBioStation Viewerについて、商用ライセンス契約を結んでおり、MIZUHO/ABINIT-MPおよびMIZUHO/BioStation Viewerとして、コンサルティングや受託解析、受託開発などの有償のサービスを提供しております。
機能
機能一覧
| 機能 | 概要 |
|---|---|
| FMO法 | FMO2法, FMO3法、FMO4法 |
| エネルギー計算 | HF法, MP2法, LMP2法, MP3法 |
| エネルギー勾配 | HF法, MP2法 |
| 基底関数 | STO-3G,および6-31G基底系、モデルコアポテンシャル (MCP)※ |
| 構造最適化 | BFGS法,CG法,PRCG法,部分構造最適化 |
| population解析 | Mulliken電荷,NBO電荷 |
| BSSE補正 | Counterpoise法 |
| IFIE解析 | フラグメント間の相互作用エネルギーを定量的に解析(FMO4法に対応) |
| PIEDA解析 | IFIEを4つのエネルギー成分(静電項、交換反発項、電荷移動項、分散項)に分解した解析 |
| IFIE map | IFIEの2次元マップによる二体相互作用の網羅的解析 |
| VISCANA | 相互作用パターンの階層的クラスター解析によるリガンド類似性の抽出 |
| CAFI | 軌道レベルの電荷移動・分極相互作用解析 |
| FILM | 軌道レベルの分散相互作用解析(CH/π, π/π相互作用等) |
| CHPI | CH/π相互作用を解析・可視化 |
| グリッドデータ解析 | 電子密度、静電ポテンシャル、分子軌道、電場ベクトル |
※MCPは、国立大学法人お茶の水女子大学 森寛敏研究室において開発されています。
動作環境
(1)MIZUHO/ABINIT-MP
| マシン環境 |
CPU: Intel® Xeon® 2.0GHz (相当) 4コア以上(16コア以上を推奨) |
|---|---|
|
メモリ:16GB以上 (1コア当たり4GB以上推奨) |
|
| HDD空き容量:10GB以上 | |
| OS | Linux (64bit版)、Windows® XP/7(64bit版) |
| その他ライブラリ | OpenMPI、Intel compiler (Math Kernel Library 付属のver. 11.0以上)が必須 |
(2)MIZUHO/BioStation Viewer
| マシン環境 | CPU:Pentium®IV 2.0GHz(相当)以上 |
|---|---|
| メモリ:1GB以上 | |
| HDD空き容量:100MB以上 | |
| グラフィックボード:VRAM256MB以上 | |
| OS | Windows® XP/7 |
* 上記は推奨動作環境の一例です。
* 「BioStation」、「ABINIT-MP」は、国立大学法人東京大学の登録商標です。
* Windows®は米国Microsoft Corporationの米国およびその他の国における登録商標または商標です。
* その他記載の製品、サービス名は、各社の登録商標または商標です。
サービス
サービス一覧
当社では、MIZUHO/BioStationの販売から保守、解析コンサルティング、カスタマイズまでのサービスの提供を通じ、創薬、バイオ、材料分野における分子設計を支援いたします。
| 導入支援 | 計算機の環境設定からMIZUHO/BioStationのインストール、操作方法についてトレーニングを行います。 |
|---|---|
| 技術サポート | MIZUHO/BioStationの操作方法に関する技術サポートを行います。対象分子のフラグメント分割や入力ファイルの設定等のノウハウについてもアドバイスします。 |
| 解析コンサルティング |
MIZUHO/BioStationを用いた受託解析を行います。 お客さまの課題解決に向けて、モデリングからシミュレーション、評価までをFMO計算の専門家がサポートします。 |
| カスタマイズ | MIZUHO/BioStationのオプションモジュールの販売やお客さまのニーズに合わせた機能追加などのカスタマイズを行います。 |
* 「BioStation」は、国立大学法人東京大学の登録商標です。
解析事例
生体高分子シミュレーション 事例
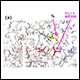
歯や骨の主成分として知られるハイドロキシアパタイト(HA)とタンパク質との親和性を解析しました。

インシリコ創薬を指向したエストロゲン受容体のリガンド結合性予測
乳がんや骨粗しょう症のターゲットタンパク質であるエストロゲン受容体を例にして、インシリコ創薬スクリーニングへのFMO量子化学計算の適用可能性を探りました。
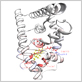
エストロゲン受容体とリガンドとの相互作用について、高精度量子化学計算による相互作用解析を行いました。リガンドと各アミノ酸残基との相互作用エネルギー、電荷移動相互作用、分散相互作用の描像が明らかになりました。

遺伝子の転写を制御するタンパク質とDNAとの特異的分子認識に関して、FMO量子化学計算により、配列特異的な相互作用メカニズムを明らかにしました。IFIE mapによる網羅的な相互作用解析も行っています。

EGFRチロシンキナーゼ阻害剤のドッキング構造、結合エネルギー解析
肺がんの分子標的薬である、チロシンキナーゼ阻害剤の候補化合物に対して、FMO量子化学計算を行い、ドッキング計算と結合エネルギー解析を行いました。
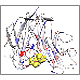
インフルエンザウイルスの膜表面タンパク質とタミフルとの相互作用について、FMO量子化学計算を行い、タミフルと周辺アミノ酸残との相互作用や薬剤耐性ウイルスとの相互作用の解析を行っています。
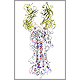
インフルエンザウイルスの膜表面タンパク質とFab抗体との抗原抗体反応について、FMO量子化学計算による相互作用解析の観点から、ウイルス変異予測を行いました。
新型インフルエンザウイルスのワクチン開発のための量子化学計算
新型インフルエンザウイルス2009H1N1/pdmのシアル酸認識に関するFMO量子化学計算を行い、特定のアミノ酸変異によって過去のウイルスよりも受容体との結合が強くなることを示しました。
生体とインプラントとの相互作用の理解のため、シリコン酸化膜表面とアミノ酸の相互作用を密度汎関数法を用いて解析しました。
タンパク質とリガンドとの相互作用解析において、水中でのタンパク質の構造揺らぎの影響を考慮することが望ましいと考えられます。小規模なタンパク質TrpCageを用いて、古典分子動力学計算とFMO量子化学計算を組み合わせた解析を行いました。
Citation
MIZUHO/BioStationを用いた成果の発表時の引用
バイオ分子相互作用シミュレータ MIZUHO/BioStationは、東京大学生産技術研究所革新的シミュレーション研究センター(CISS)にて管理・公開するプロジェクトの成果の使用許諾を受け、当社が改変・販売している商用ソフトウェアです。
MIZUHO/BioStationを用いた成果を発表する際は以下の例のように使用したソフトウェアの名前、バージョン、著作権者氏名などを明示してください。
【記載例】
英文)
ABINIT-MP 5.0 and BioStation Viewer 13.01 (MIZUHO Rev.), Tatsuya Nakano, Yuji Mochizuki, et al., Research and Development of Innovative Simulation Software, 2011.
和文)
ABINIT-MP 5.0 and BioStation Viewer 13.01 (MIZUHO Rev.),中野達也, 望月祐志ら,イノベーション基盤シミュレーションソフトウェアの研究開発,2011.
SERVICE MENU
本サービスでは以下のメニューをご提供します。
-
数値解析



